
Notre recherche
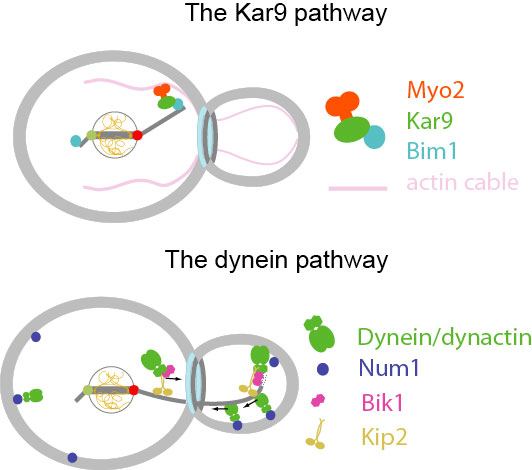
La division cellulaire asymétrique est le type de division principalement utilisé par les cellules souches et joue un rôle central dans la création de la diversité au cours du développement des organismes pluricellulaires. Lors de certaines divisions cellulaires, les déterminants d’identité cellulaire sont ségrégés asymétriquement entre les cellules filles. La position du fuseau mitotique dans le noyau cellulaire détermine si la cellule se divise de façon symétrique ou asymétrique. A son tour, le positionnement du fuseau dépend des interactions entre les microtubules et des facteurs corticaux. Un réseau complexe de protéines, incluant des protéines non-motrices associées aux microtubules (plus-end tracking proteins, +TIPs), des moteurs moléculaires (kinèsines et dynéine) et des protéines interagissant avec l’actine, est impliqué dans ces interactions.
La levure bourgeonnante est utilisée comme organisme modèle pour étudier la division cellulaire asymétrique. Le positionnement du fuseau dans la levure est régulé par deux voies génétiquement identifiées, qui sont des médiateurs universels du positionnement du fuseau pendant la division cellulaire asymétrique chez les eucaryotes. Cependant, leur régulation n’est pas bien comprise.
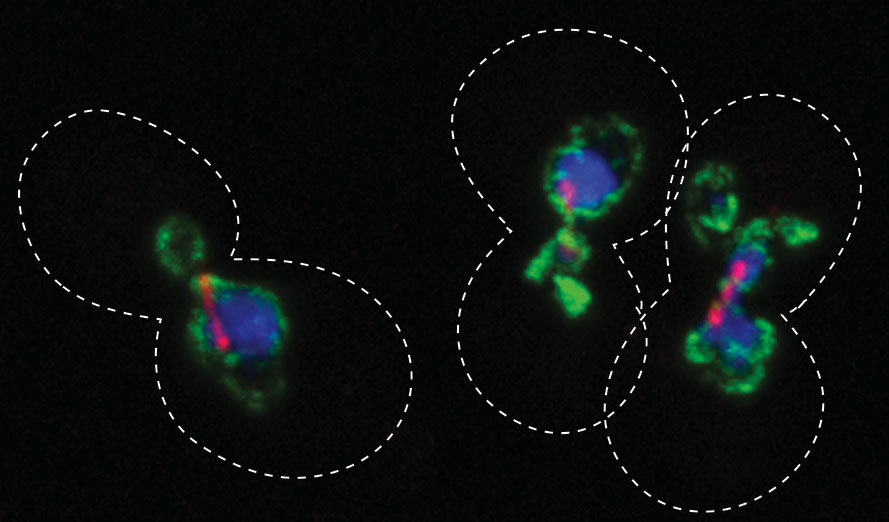
Nous cherchons à comprendre comment des régulateurs du cycle cellulaire peuvent contrôler les médiateurs du positionnement du fuseau ainsi que les autres processus du cytosquelette, par exemple, la ségrégation des chromosomes et la cytokinèse. Pour cela, nous utilisons des approches génétiques, biochimiques/biophysiques et de la vidéo-microscopie à fluorescence.
En savoir plus
Financements
ANR (Didier Portran)
Publications
2023
- The motor domain of the kinesin Kip2 promotes microtubule polymerization at microtubule tips. Chen X, Portran D, Widmer LA, Stangier MM, Czub MP, Liakopoulos D, Stelling J, Steinmetz MO, Barral Y. J Cell Biol. 2023 Jul 3;222(7):e202110126. Pubmed
2021
- Coupling DNA Replication and Spindle Function in Saccharomyces cerevisiae. Liakopoulos D. Cells. 2021 Nov 30;10(12):3359. Pubmed
2019
- How Does SUMO Participate in Spindle Organization? Abrieu A, Liakopoulos D. Cells. 8(8). Pubmed
- Lattice defects induce microtubule self-renewal. Schaedel L, Triclin S, Chrétien D, Abrieu A, Aumeier C, Gaillard J, Blanchoin L, Théry M, John K.. Nat Phys. 2019 Aug;15(8):830-838. Pubmed
2018
- An E2-ubiquitin thioester-driven approach to identify substrates modified with ubiquitin and ubiquitin-like molecules. Bakos G, Yu L, Gak IA, Roumeliotis TI, Liakopoulos D, Choudhary JS, Mansfeld J. Nat Commun. 9(1):4776. Pubmed
2016
- Kar9 controls the nucleocytoplasmic distribution of yeast EB1. J. Schweiggert, D. Panigada, AN. Tan, D. Liakopoulos Cell Cycle, 15 : 2860-2866. Pubmed
- Regulation of a Spindle Positioning Factor at Kinetochores by SUMO-Targeted Ubiquitin Ligases. Schweiggert J, Stevermann L, Panigada D, Kammerer D, Liakopoulos D. Dev Cell. 36:415-27. Pubmed
2015
- Kinesin Kip2 enhances microtubule growth in vitro through length-dependent feedback on polymerization and catastrophe. Hibbel A, Bogdanova A, Mahamdeh M, Jannasch A, Storch M, Schäffer E, Liakopoulos D, Howard J. Elife. 4: e10542. Pubmed
2013
- An auxiliary, membrane-based mechanism for nuclear migration in budding yeast. Kirchenbauer M, Liakopoulos D. Mol Biol Cell. 24(9):1434-43. Pubmed
2010
- Ubiquitylation regulates interactions of astral microtubules with the cleavage apparatus. Kammerer D, Stevermann L, Liakopoulos D. Curr Biol. 20(14):1233-43. Pubmed
- Arp1, an actin-related protein, in Plasmodium berghei. Siden-Kiamos I, Schüler H, Liakopoulos D, Louis C. Mol Biochem Parasitol. 173(2):88-96. Pubmed
2008
- Regulation of mitotic spindle asymmetry by SUMO and the spindle-assembly checkpoint in yeast. Leisner C, Kammerer D, Denoth A, Britschi M, Barral Y, Liakopoulos D. Curr Biol. 18(16):1249-55. Pubmed
Organisation et positionnement du fuseau mitotique

Dimitris LIAKOPOULOS
Chef d’équipe (Chercheur DR2 CNRS)
Membres de l’équipe
(Chercheur DR2) +33 (0)4 34 35 95 36 |
|
(Chercheur DR2) +33 (0)4 34 35 95 67 |
|
(IE-Recherche) +33 (0)4 34 35 95 67 |
|
(CRCN) +33 (0)4 34 35 96 43 |
|
(Doctorant) +33 (0)4 34 35 95 67 |

Contactez notre équipe
Remplacez le nom et l’adresse ci-dessus par celui du membre à contacter
prenom.nom@crbm.cnrs.fr






